- 박현규 교수 연구팀, RNA 바이러스 초고감도 검출 기술 개발
- 관리자 |
- 2021-07-19 14:57:01|
- 955
- 2021-07-19 14:57:01|
- 관련보도링크
(NESBA, Nicking and Extension chain reaction System-Based Amplification) 기술 개발
▶ 아래 내용은 우리학교 홍보실에서 작성하여 학교 홈페이지에 게시한 자료입니다.
▶ 관련 연구성과 소식이 2021년 7월 15일 헤럴드경제, 서울경제, 전자신문, 이데일리 등 여러 언론매체를 통해 소개 되었습니다.

< (왼쪽부터) 생명화학공학과 박현규 교수, 주용 박사과정 >
우리 대학 생명화학공학과 박현규 교수 연구팀이 핵산의 절단 및 중합 연쇄반응 시스템을 활용해 RNA 바이러스의 표적 RNA를 초고감도로 검출하는
새로운 등온 핵산 증폭(NESBA, Nicking and Extension chain reaction System-Based Amplification) 기술을 개발했다고 15일 밝혔다.
생명화학공학과 주용 박사과정, 김효용 박사가 공동 제1 저자로 참여한 이번 연구는 영국 왕립화학회가 발행하는 국제학술지 `나노스케일 (Nanoscale)'에
2021년도 24호 표지(Front cover) 논문으로 지난달 16일 선정됐다. (논문명: Ultrasensitive version of nucleic acid sequence-based amplification (NASBA)
utilizing nicking and extension chain reaction system)
현재 전 세계적으로 팬데믹 (Pandemic)을 일으키고 있는 코로나19 바이러스와 같은 RNA 바이러스를 검출하기 위한 표준 진단 방법은 역전사 중합효소 연쇄반응(qRT-PCR)이다.
이러한 표준 분자진단 방법은 면역진단 방법과 비교해 진단의 정확도는 매우 우수하지만 정교한 온도 조절 장치가 필요하고 진단에 드는 시간이 길어 장비의 소형화에
제약이 있으며 전문 진단 설비가 갖추어진 대형 병원 또는 전문 임상검사실에서만 제한적으로 사용된다는 단점이 있다.
연구팀은 이러한 현행 기술의 한계를 극복하기 위해 핵산의 절단 및 중합 연쇄반응 시스템에 의해 구동되는 초고감도의 신개념 등온 핵산 증폭 기술을 개발했으며,
이를 통해 별도의 온도 변환 과정 없이 동일 온도에서 표적 바이러스의 RNA를 초고감도로(검출 한계: 1 아토 몰 (aM)) 매우 신속하게(20분 이내) 검출하는 데 성공했다.
연구팀은 기존 나스바(NASBA, Nucleic Acid Sequence-Based Amplification) 등온 증폭 기술에 절단효소 인식 염기서열이 수식된 프라이머를 도입함으로써, 절단효소 및
DNA 중합효소 활성을 기반으로 T7 프로모터를 포함하는 이중가닥 DNA를 지수함수적으로 증폭할 수 있었고, 최종적으로 표적 RNA를 기존의 NASBA 기술에 비해
100배 이상 향상된 민감도로 검출할 수 있었다.
연구팀은 이 기술을 통해서, 호흡기 세포 융합 바이러스(RSV)의 유전 RNA(genomic RNA)를 별도의 전처리 없이 매우 신속하고 고감도로 검출함으로써,
기술의 실용성을 증명함과 동시에 현장 검사(POCT) 기술로서의 높은 활용 가능성을 입증했다.
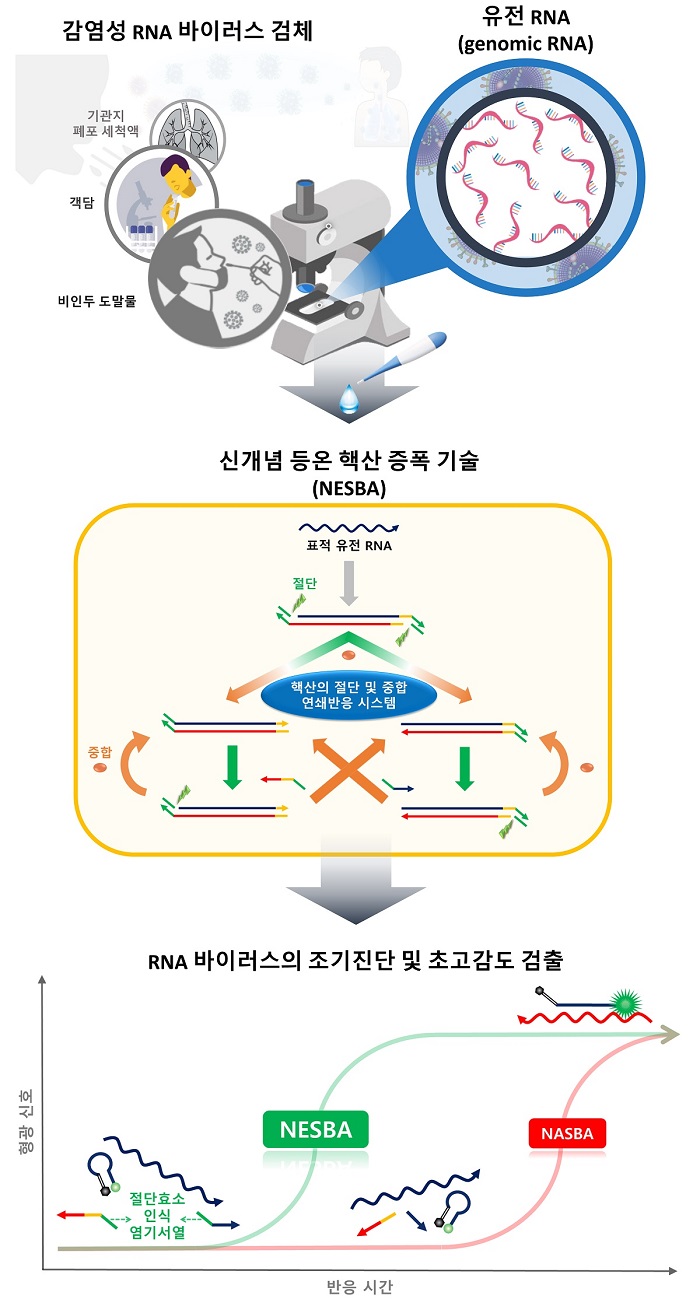
< 그림 1. RNA 바이러스 초고감도 검출 기술 연구 모식도 >
박현규 교수는 "이번 신개념 등온 핵산 증폭 기술은 현재 대유행하고 있는 코로나19 바이러스와 같은 RNA 바이러스들을 신속하게 조기 진단 할 수 있는
분자진단 시스템에 활용될 가능성이 매우 큰 기술ˮ이라고 이번 연구의 의의를 설명했으며, 현재 코로나19의 임상 샘플 테스트에서도 매우 좋은 결과를 얻었다고 언급했다.
한편 이번 연구는 한국연구재단의 글로벌 프런티어사업과 경남제약(주)의 연구비 지원으로 수행됐다.

< 그림 2. 논문 커버 이미지 >
- 이전
- 이상엽 특훈교수 교수 연구팀, 살아있는 미생물 내 바이오 플라스틱 생성 관찰 최초 성공
- 2021-07-30
- 다음
- 제18회 이산화탄소 활용에 관한 국제학술대회 개최(ICCDU 7.18(Sun)~22(Thu))
- 2021-07-19

